Luigi Ricciardi 1 , Rosa Mazzeo 2,*©, Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1 © en Concetta Lotti 2,*
- 1 Departement Grond-, Plant- en Voedselwetenskappe, Plantgenetika en Teeleenheid Universiteit van Bari, Via Amendola 165/A, 70125 Bari, Italië; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (ARM); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Departement van die Wetenskappe van Landbou, Voedsel en Omgewing, Universiteit van Foggia, Via Napoli 25, 71122 Foggia, Italië
- 3 Departement Biowetenskappe, Biotegnologie en Biofarmaseutika, Universiteit van Bari, Via Orabona 4, 70125 Bari, Italië; guglielmo.rainaldi@uniba.it
- 4 Departement van Energietegnologieë, Bio-energie, Bioraffinadery en Groen Chemie Afdeling, ENEA Trisaia Navorsingsentrum, SS 106 Ionica, km 419+500, 75026 Rotondella (MT), Italië; paolo.iovieno@enea.it
* korrespondensie: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
Opsomming:
Ui (Allium cepa L.) is die tweede belangrikste groentegewas wêreldwyd en word wyd waardeer vir sy gesondheidsvoordele. Ten spyte van sy beduidende ekonomiese belangrikheid en sy waarde as funksionele voedsel, is uie swak ondersoek met betrekking tot sy genetiese diversiteit. Hierin het ons die genetiese variasie in die "Acquaviva rooi ui" (ARO), 'n landras met 'n eeu-oue geskiedenis van verbouing in 'n klein dorpie in die provinsie Bari (Apulië, Suid-Italië) ondersoek. 'n Stel van 11 mikrosatellietmerkers is gebruik om die genetiese variasie in 'n kiemplasmaversameling wat uit 13 ARO-populasies en drie algemene kommersiële tipes bestaan, te ondersoek. Ontledings van genetiese struktuur met parametriese en nie-parametriese metodes het uitgelig dat die ARO 'n goed gedefinieerde genepoel verteenwoordig, duidelik onderskei van die Tropea- en Montoro-landrasse waarmee dit dikwels verwar word. Om 'n beskrywing te gee van bolle wat gewoonlik vir vars verbruik gebruik word, is die inhoud van oplosbare vastestof en skerpheid geëvalueer, wat hoër soetheid in die ARO toon met betrekking tot die twee bogenoemde landrasse. Oor die algemeen is die huidige studie nuttig vir die toekomstige valorisering van die ARO, wat bevorder kan word deur kwaliteit etikette wat kan bydra om kommersiële bedrog te beperk en die inkomste van kleinboere te verbeter.
Inleiding
Die Allium-genus sluit ongeveer 750 spesies [1] in, waaronder uie (Allium cepa L., 2n = 2x =16) een van die mees wydverspreide is. A. cepa het 'n tweejaarlikse siklus en oorskry voortplantingsgedrag. Deesdae maak uie wêreldwye produksie (97.9 Mt) dit die tweede belangrikste groentegewas na tamatie [2]. Sedert ou tye is uiebolle beide as voedsel en in volksmedisinale toepassings gebruik. Inderdaad, antieke Egiptenare het reeds verskeie terapeutiese formules gerapporteer wat gebaseer is op die gebruik van knoffel en uie in 'n mediese papirus van die 1550 vC, die Codex Ebers [3].
Hierdie veelsydige en gesonde groente word rou, vars of as verwerkte produk verteer en gebruik om die smaak van baie geregte te verbeter. Verskeie onlangse studies beweer dat uieverbruik die risiko van kardiovaskulêre siektes [4,5], vetsug [6], diabetes [7] en verskeie vorme van kanker kan verminder [8-10]. Eienskappe van uiegesondheid word dikwels toegeskryf aan hoë vlakke van twee klasse nutraceutiese verbindings: flavonoïede en alk(en)yl-sisteïensulfoksiede (ACSO's). Die eerste klas sluit flavonole en antosianiene in. Quercetin is die belangrikste waarneembare flavonol, bekend vir sy sterk antioksidante en anti-inflammatoriese eienskappe in vrye radikale opruiming en oorgangsmetaalione binding [11]; terwyl antosianiene rooi/pers kleur aan sommige uievariëteite verleen. Wat ACSO's betref, is die volopste isoallien [(+)-trans-S-1-propeniel-L-sisteïensulfoksied] [12], 'n nie-vlugtige en nie-proteïenogeniese swaelaminosuur wat in die selle gestoor word, wat indirek verantwoordelik is vir die skerp aroma en smaak van uie [13]. By weefselontwrigting, word isoalien deur die ensiem alliinase gesplit om 'n reeks vlugtige verbindings (piruvaat, ammoniak, tiosulfonate en propanetiese S-oksied) te produseer wat skeur veroorsaak en onaangename reuk (pragtigheid) veroorsaak. [14]. Die uie skerpheid word dikwels gemeet as die hoeveelheid, per gram vars gewig, pirodruivensuur wat deur hidrolise gegenereer word [15.16].
In die lande van die Middellandse See-bekken, voorgestel as een van die sekondêre diversiteit sentrums van A. cepa [17.18], uiebolle vertoon 'n wye variasie in vorm, grootte, kleur, droëmateriaal en skerpheid [19-22]. Boonop kan swaelgebaseerde bemesting, agronomiese praktyke, tipe grond, klimaatstoestande en die genotipe van kultivars of landrasse die bolgehalte beïnvloed deur eienaardige organoleptiese en voedingswaardes te verleen. [23-27]. In Italië, ten spyte van die wye uie-kiemplasma-beskikbaarheid, word slegs 'n paar uievariëteite dikwels aan wetenskaplike studies onderwerp en behoorlik gekarakteriseer. [28.29].
Deeglike genetiese en fenotipiese karakterisering van agro-biodiversiteit is van kardinale belang om toepaslike bewaring van plantgenetiese hulpbronne te verseker en die gebruik van spesifieke genotipes in die waardeketting te bevorder [30-32]. Simple sequence repeat (SSR) merkers is dikwels gekies vir kartering [33-35], DNS-vingerafdrukke en kultivar-diskriminasie [36-38], en betroubare skatting van genetiese veranderlikheid binne en tussen landrasse [39-42], aangesien hulle lokusspesifiek, multi-allelies, kodominant oorgeërf, hoogs reproduseerbaar is en geskik is vir geoutomatiseerde genotipering.
In die huidige studie het ons ons aandag gevestig op 'n Apuliese tradisionele landras, die "Acquaviva rooi ui" (ARO), wat volgens organiese boerderymetodes verbou word in 'n klein area van die dorp Acquaviva delle Fonti, in die provinsie Bari (Apulië, Suid-Italië). Die bolle van hierdie landras is groot en plat en rooikleurig en word grootliks in plaaslike resepte gebruik. Alhoewel die ARO die “Slow Food Presidium”-gehaltemerk verwerf het, kan die produksie daarvan verder bevorder en beskerm word deur Europese Unie-gehaltemerke soos beskermde geografiese aanduiding (BGA) en beskermde oorsprongsbenaming (POD), aangesien dit kan bydra om die kommersiële bedrog en die inkomste van kleinboere te verbeter. Hierin is SSR molekulêre merkers gebruik as kragtige instrumente om genetiese variasie onder ARO bevolkings te bepaal en om hierdie landras van ander twee Suid-Italiaanse rooi uie landrasse te onderskei. Verder het ons skerpheid en oplosbare vastestof-inhoud beraam om ARO-geur in verhouding met die markvraag te evalueer.
Results
Vestiging van Acquaviva Rooi Ui-kiemplasmaversameling en morfologiese karakterisering
Saad van 13 bevolkings van die ARO-landras, geskenk deur boere in die raamwerk van die BiodiverSO Apulia-streek-projek, is gebruik om 'n ARO-kiemplasmaversameling te vestig.
Morfologiese beskrywers, verwant aan bol, vel en vleis is versamel op ARO-kiemplasma en op drie uie landrasse, twee wat aan die "Tropea rooi ui" (TRO) landras behoort en een aan die "Montoro koper ui" (MCO) landras (Figuur) 1). Al die ARO-bolle was plat en is gekenmerk deur rooi uitwendige vel en vleis met verskillende skakerings van rooi. Daarteenoor was die vleis van TRO-bolle heeltemal rooi, terwyl die vleis van MCO-bolle swak gepigmenteer was (Tabel S1). Biochemiese analise het toegelaat om die vastestof oplosbare inhoud en skerpheid te evalueer. Soos gerapporteer in Tabel 1, die gemiddelde waardes van vastestof oplosbare inhoud van bolle in ARO populasies was 7.60, en het gewissel van 6.00 (ARO12) tot 9.50° Brix (ARO11 en ARO13). Hierdie waarde was hoër as die een wat vir die TRO- en MCO-landrasse beraam is (onderskeidelik 4.25 en 6.00° Brix).

Tabel 1. Vaste oplosbare inhoud en skerpheidswaardes geassesseer in "Acquaviva Rooi Ui" (ARO), "Tropea Rooi Ui" (TRO), en "Montoro Koper Ui" (MCO) populasies *.
| KODE | Oplosbare vaste inhoud (Brix) | skerpheid (pmolg-1 FW) | ||
| beteken | CV y (%) | beteken | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 die | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28ab | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 die | 3.74 |
| ARO 5 | 7.50 BCD | 0.00 | 6.80 die | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 die | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 die | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94ab | 6.57 |
| ARO11 | Die 9.50 | 7.44 | 5.54ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91ab | 9.70 |
| ARO13 | Die 9.50 | 7.44 | 6.63 die | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18ab | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 b | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28ab | 4.79 |
* Betekenis met dieselfde letters in hoofletters of kleinletters verskil nie statisties by 0.01P of 0.05P onderskeidelik nie (SNK se toets). y Koeffisient van variasie.
Die gemiddelde waarde van ARO skerpheid, geassesseer deur middel van pirodruivensuurinhoud, was 6.00, het gewissel van 4.51 pmol g-1 FW (ARO6) tot 7.04 (ARO8). Hierdie waarde was hoër as die een wat in TRO- en MCO-landrasse geskat is (3.54 pmol g-1 FW en 4.18 pmol g-1 FW, onderskeidelik).
SSR Polimorfisme en Genetiese Verwantskappe tussen Toetredings
In die huidige studie het 11 uit 37 getoetste SSR-primerkombinasies enkel-lokus polimorfismes verskaf, dit wil sê, wat hoogstens twee amplifikasieprodukte in 'n enkele individu oplewer. In die geheel is 55 allele in 320 individue opgespoor met 'n aantal allele per lokus wat wissel van 2 (ACM147 en ACM 504) tot 11 (ACM132) en 'n gemiddelde waarde van 5 allele (tabel) 2). In individuele populasies het die aantal allele (Na) gewissel van 1.94 (ACM147 en ACM504) tot 5.38 (ACM132), terwyl die effektiewe aantal allele (Ne) van 1.41 (ACM152) tot 2.82 (ACM449) gewissel het. Teenstrydighede tussen Na- en Ne-waardes was te wyte aan die teenwoordigheid van allele met lae frekwensie in die populasies en die oorheersing van slegs 'n paar allele. Die hoogste waargenome heterosigositeit (Ho) waarde is uitgelig vir ACM138 en ACM449 (0.62), terwyl die laagste een met ACM152 (0.25) geassosieer is. Verwagte heterosigositeit (He), wat ooreenstem met die teoretiese verwagting in 'n panmiktiese populasie, het gewissel van 0.37 (ACM504) tot 0.61 (ACM132, ACM138 en ACM449). Die Wright se fiksasie-indeks (Fis), het waardes naby aan nul (gemiddeld 0.05) vir al die merkers vertoon, wat soortgelyke waardes tussen waargenome en verwagte heterosigositeitsvlakke aandui, soos verwag vir 'n uitkruisende spesie. Die doeltreffendheid van individuele SSR merker in genetiese vingerafdrukke is beraam deur die polimorfiese inligting inhoud (PIC) indeks, met 'n gemiddelde waarde van 0.48 en het gewissel van 0.33 (ACM504) tot 0.67 (ACM132). Nog 'n doeltreffendheidsindeks, die Shannon's Information Index (I), het 'n gemiddelde waarde van 0.84 vertoon, en aangeneemde waardes het gewissel van 0.45 (ACM152) tot 1.20 (ACM132).
Tabel 2. Polimorfisme-kenmerke van die 11 SSR-merkers wat gebruik word om genetiese diversiteit in ARO-, TRO- en MCO-bevolkings te skat. Totale aantal allele (Na), bandgroottereeks en polimorfiese inligtinginhoud (PIC)-indeks Verwys na die totale stel van 320 individue wat in hierdie studie genotipeer is. Aantal allele (Na), aantal effektiewe allele (Ne), waargenome heterosigositeit (Ho), verwagte heterosigositeit (He), fiksasie-indeks (Fis), en Shannon se inligtingsindeks (I) verwys na gemiddelde waardes bereken uit 16 populasies, elk saamgestel deur 20 individue.
| Lokus. | Totaal Na | Groottereeks (bp) | PIC | beteken | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| beteken | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Onder die populasies het ARO3, ARO6, ARO8, ARO10, TRO1 en MCO hoë vlak van genetiese variasie (Ho > 0.5) vertoon, terwyl die laagste diversiteit in die populasie ARO7 (Ho = 0.27) waargeneem is (Aanvullende Tabel S2). In die algemeen het al die toetredings Fis waardes naby aan nul (Fis gemiddelde waarde = 0.054), soos verwag onder ewekansige paringstoestande.
Ontleding van molekulêre variansie en genetiese struktuur
Hiërargiese verdeling van genetiese variasie tussen en binne populasies is deur AMOVA bereken. Die resultate het 'n aansienlike fraksie van genetiese variasie binne populasies uitgelig (87%). Variasie tussen bevolkings, 13%, was hoogs betekenisvol (P < 0.001) (Tabel 3). Paarsgewyse waardes van die Fpt-parameter, 'n analoog van die Wright se Fst-fiksasie-indeks, wat wissel van 0.002 (ARO2/ARO10) tot 0.468 (ARO7/TRO2), was betekenisvol (P < 0.05), behalwe vir nege paarsgewyse vergelykings (Aanvullende Tabel S3).
Tabel 3. Ontleding van molekulêre variansie van 320 genotipes van 16 populasies van allium cepa L.
| Bron | df | Som van vierkante | Variansieskatting | Variansie (%) | Fpt | P |
| Onder bevolkings | 15 | 458.63 | 1.16 | 13% | ||
| Binne bevolkings | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| Totaal | 319 | 2731.62 | 8.66 |
Ondersoek van genetiese struktuur in die A. cepa versameling wat in hierdie studie gegentipeer is, is uitgevoer deur middel van die mengselmodel-gebaseerde groeperingsanalise wat in die sagteware STRUKTUUR geïmplementeer is. Die Evanno AK-metode het onderverdeling in twee trosse (K = 2) voorgestel as die mees insiggewende vir ons dataset,met the volgende hoogste peak by K = 5 (supplementaiv Rgure S1). Die vir K = 2, ahpopulasies were gatigned ooknenf die twee trosse met 'n rnernbertoip-koëffisiënt (q) > 0.7. Soos shown in Figuur 2a, het die eerste groepering (genoem S1) MCO en alle ARO-populasies ingesluit, terwyl die S2-kluster die twee TRO-populasies gegroepeer het. By K = 5, verskaf 'n dieper beskrywing van die datastel (Figuur 2b), 75% van die toetredings is aan een van die vyf groeperinge toegewys. Skeiding tussen ARO (S1) en TRO (S2) is bevestig, alhoewel sommige ARO-populasies gemeng is (q < 0.7) of afsonderlik in die twee nuwe trosse S3 en S4 (ARO7 en ARO12, onderskeidelik) gegroepeer is. Interessant genoeg het die MCO kommersiële tipe 'n duidelike groep (S5) geskei van die Apuliese rooi ui gevorm.
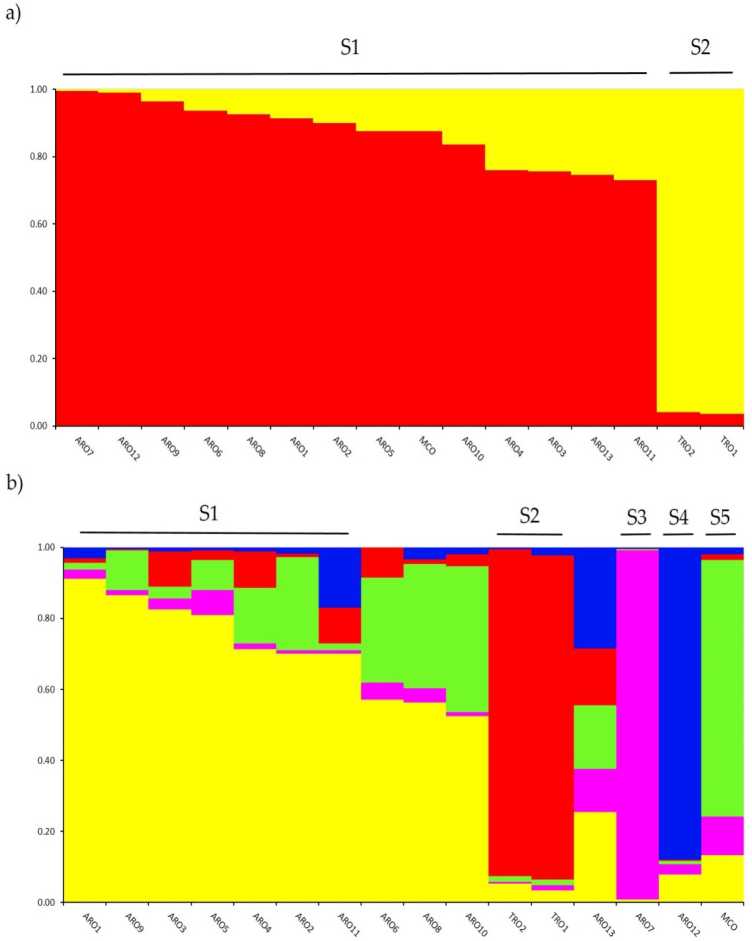
Genetiese Verwantskappe tussen Bevolkings
SSR-polimorfisme het toegelaat om 'n dendrogram van genetiese diversiteit te teken en die resultate van die filogenetiese analise word in Figuur getoon 3a. Hier is die kiemplasmaversameling in vyf groepe verdeel wat sterk deur selflaai-waardes ondersteun word. Die ARO7- en ARO12-populasies is onmiddellik van die oorblywende bevolkings geskei en het twee afsonderlike trosse gevorm. Die derde groepering het die twee kommersiële populasies van TRO ingesluit, intussen het die vierde nodus MCO van elf ARO-populasies verdeel. Genetiese verwantskap wat tussen populasies voorkom, is verder ondersoek deur middel van hoofkoördinaatanalise (PCoA) (Figuur 3b). Soos voorheen uitgelig, is ARO populasies styf gegroepeer, behalwe vir ARO12 en ARO7, wat in geïsoleerde posisies in die PCoA plot verskyn het. Die twee TRO's en die MCO-bevolkings was in die onderste regterkantste paneel van die plot versprei.
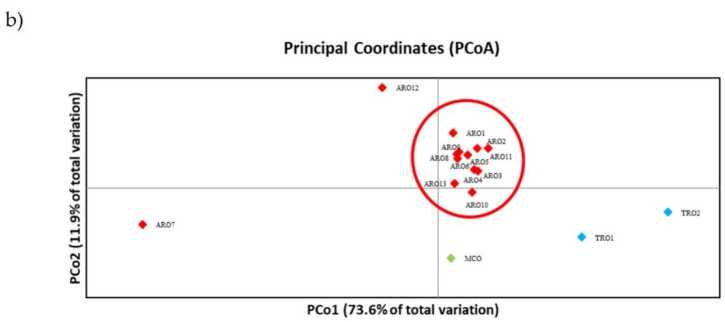
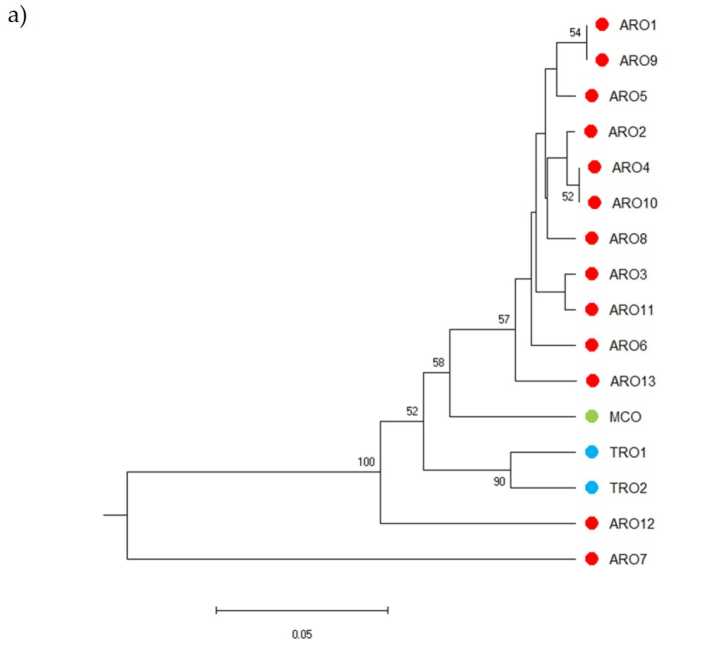
Figuur 3. Genetiese diversiteit onder 16 A. cepa populasies wat in hierdie studie gekarakteriseer is, gebaseer op hul SSR-profiel. (a) UPGMA dendrogram van genetiese afstand. Bootstrap-ondersteuningswaardes >50 word bo die ooreenstemmende nodusse aangedui; (b) hoofkomponent-analise (PCoA). Die groep het in rooi omsirkel, wat ten volle ooreenstem met die groep wat deur filogenetiese analise gegenereer is en bestaan uit 11 ARO-toetredings.
Bespreking
Binne die groot hoeveelheid agro-biodiversiteit wat tradisioneel in Suid-Italië verbou word, verteenwoordig uielandrasse nisprodukte wat bewaar moet word teen die risiko van genetiese erosie en die bedreiging van vervanging deur moderne kultivars. In die raamwerk van die streekprojek BiodiverSO, wat daarop gemik is om genetiese hulpbronne van die Apulië-streek wat sterk gekoppel is aan plaaslike erfenis te versamel, te karakteriseer, te bevorder en te beskerm, het ons 'n saadversameling van 13 bevolkings van die ARO-landras gevestig. Ons het die eerste assessering van ARO-variasie in terme van DNS-polimorfismes en twee biochemiese parameters, oplosbare vastestof en pirodruivensuurinhoud, gerapporteer, wat verband hou met geureienskappe en van belang vir die aanvaarding van die vars ongekookte produkte. Daarbenewens is data oor die ARO-landras vergelyk met dié wat ingesamel is op twee ander gepigmenteerde uie-landrasse waarmee dit dikwels verkeerd was.
Biochemiese ontledings het die soetheid van die 13 ARO-bevolkings uitgelig, verwant aan hoë oplosbare vastestofinhoud en medium skerpheid, volgens die riglyne vir die soet uiebedryf [31]. ARO-bolle was soeter as dié van die TRO- en MCO-landrasse, en het 'n effens hoër skerpheid getoon. Soetheid in uie is egter te danke aan 'n balans tussen suikerinhoud en skerpheid, daarom kan hierdie karakterisering nuttig wees om die seleksie van genotipes van waarde te ondersteun, wat gewoonlik deur boere slegs op grond van die morfologie uitgevoer word.
SSR-merkers is bevestig as 'n nuttige hulpmiddel om genotipes te onderskei, al is dit binne 'n nou groeiende gebied soos die dorp Acquaviva delle Fonti versamel. Die geselekteerde merkers het 'n groter aantal allele vertoon as die merkers wat voorheen deur gerapporteer is [43] en [44], maar laer as die merkers gerapporteer deur [45]. Boonop het 50% van ons stel merkers PIC-indekswaardes groter as 0.5 getoon, wat geskik is om die populasies in die versameling te diskrimineer, soos voorgestel deur [46]. Assessering van diversiteit binne bevolkings het soortgelyke waardes tussen Ho en He geopenbaar, wat gelei het tot lae Fis waardes. Dit is in ooreenstemming met die uitkruising aard van A. cepa, wat ernstig aan inteeltdepressie ly [47]. Die algehele Fis waarde bereken in uiebevolkings wat in hierdie studie oorweeg is (0.054) was laer as die een wat voorheen gerapporteer is deur [45] (0.22) en amper identies aan die een gevind deur [31] (0.08) en [48] (0.00) wat genetiese diversiteit in uielandrasse van onderskeidelik noordwes Spanje en Niger beoordeel het. Opmerklike vlakke van heterosigositeit in ARO-bevolkings versterk die idee dat Apulië 'n diversiteitsentrum vir baie tuinbouspesies verteenwoordig [32, 42, 49-51].
AMOVA het uitgelig dat die meeste molekulêre variasie in die versameling wat in hierdie studie gegentipeer is, binne die populasies lê. Beduidende genetiese differensiasie tussen bevolkings (FPT waardes) het die voorkoms van genetiese stratifikasie aan die lig gebring. Trouens, alhoewel ons resultate die teenwoordigheid van genetiese eenvormigheid in die meeste ARO-populasies aangedui het, wat 'n goed gedefinieerde groepering vorm, het die ARO7- en ARO12-populasies 'n duidelik onderskeibare genetiese profiel vertoon. Hierdie resultaat kan wees as gevolg van 'n ander oorsprong van sade wat gebruik is deur die twee boere waaruit die bevolkings versamel is. Verder, gebaseer op die resultate wat verkry is, kan die ARO-landras beskou word as duidelik onderskeibaar op genetiese vlak van die TRO- en MCO-landrasse. In 'n onlangse studie, [29] die genetiese diversiteit van verskeie Italiaanse uie-landrasse, insluitend "Acquaviva", "Tropea" en "Montoro" beoordeel. Alhoewel die skrywers SNP-merkers gebruik het om die genetiese diversiteit van 'n wyer uieversameling te assesseer, was die genotipering nie in staat om "Acquaviva" van "Tropea" en "Montoro" uie te onderskei nie. Waarskynlik is hierdie teenstrydigheid te wyte aan die lae gemiddelde PIC-waarde wat gevind is (0.292), wat 'n beskeie algemene informatiefheid van die lokusse onder analise voorstel, soos beweer deur [29]. Verder, om die teenwoordigheid van sub-struktuur in hul Italiaanse cluster te ondersoek, sou dit beter gewees het om die Italiaanse genotipes afsonderlik van die res van die versameling te ontleed. Waarskynlik sou dit toegelaat het om patroon van genetiese diversiteit te visualiseer wat gekoppel is aan geografiese stratifikasie of eienskappe onder empiriese seleksie.
Ten slotte verteenwoordig die huidige studie 'n omvattende verslag oor 'n uielandras wat met plaaslike kulturele erfenis geassosieer word en van ekonomiese belang vir die boere. Ons resultate beklemtoon dat, met 'n paar uitsonderings, ARO gekenmerk word deur 'n goed gedefinieerde geenpoel, wat verdien om teen die risiko van genetiese erosie bewaar te word. Daarom was die vestiging van 'n verteenwoordigende versameling van hierdie waardevolle bron van genetiese diversiteit van kardinale belang. Laastens kan die genetiese en fenotipiese karakterisering van ARO nuttig wees om kwaliteitmerke van die Europese Unie te verkry.
Materiaal en metodes
Kiemplasmaversameling, plantmateriaal en DNA-ekstraksie
'n Stel van 13 bevolkings van die ARO-landras is verkry binne die raamwerk van 'n Apulië-streekprojek (BiodiverSO: https://www.biodiversitapuglia.it/), deur 'n reeks sendings wat uitgevoer is in "Acquaviva delle Fonti", 'n klein Apuliese dorpie in die provinsie Bari, Italië. Versamelplekke van elke toetreding is gekarteer deur die Geografiese Inligtingstelsel (GIS) en in tabel gerapporteer 4. Daarbenewens is twee populasies van die TRO-landras en een populasie van die MCO-landras by die huidige studie ingesluit en as verwysings gebruik. Al die plantmateriaal is in dieselfde omgewingstoestande by die proefplaas “P Martucci” van die Universiteit van Bari (41° 1'22.08″ N, 16°54'25.95″ O), onder beskermingshok gekweek om kruisbestuiwing te voorkom bevolkings en die versekering van intra-populasie bestuiwing deur middel van brommers (Lucilia caesar). Die 16 populasies is gekarakteriseer vir eienskappe wat verband hou met bolgrootte en vorm en vel- en vleeskleur (Tabel S1). Daarbenewens is vaste oplosbare inhoud-toets uitgevoer met behulp van 'n handrefraktometer en skerpheid is gemeet in uiesapmonsters wat 2,4-dinitrofenielhidrasien (0.125% bygevoeg het) v/v in 2N HCl) en evalueer absorbansie by 420 nm, soos gerapporteer deur [31]. Die Duncan se meervoudige reeks toets en die SNK toets is uitgevoer om die teenwoordigheid van beduidende verskille te bepaal.
Tabel 4. Lys van bevolkings wat in hierdie studie versamel en genotipeer is. Vir elke bevolking word identifikasiekode, plaaslike naam, GPS-koördinaat en geenbank gerapporteer wat die saad bewaar.
| kode | Naam | GPS-koördinate | Gene Bank y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54"51.372″ N 16°49"3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52"49.8″ N 16°49"48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Departement Grond-, Plant- en Voedselwetenskappe, Universiteit van Bari. |
Blaarmateriaal van 20 genotipes per populasie is gemonster en by -80 °C gestoor tot gebruik. Vir polisakkariedryke spesies, soos A. cepa, eerste stappe om polisakkaried te verwyder is noodsaaklik om goeie kwaliteit DNA te verkry, daarom is aanvanklike wassings in STE buffer (0.25 M sukrose, 0.03 M Tris, 0.05 M EDTA) uitgevoer soos beskryf deur [52]. Totale DNA is onttrek volgens die CTAB metode [53] en uiteindelik is dit nagegaan vir kwaliteit en konsentrasie deur Nano Drop 2000 UV-vis spektrofotometer (ThermoScientific, Waltham, MA, VSA) en 0.8% agarose gel elektroforese.
SSR analise
16 EST-SSR primer kombinasies ontwikkel deur [54] en voorheen getoets in genetiese diversiteitstudies deur [43] en [44] en 21 genomiese SSR [45-55] is gekeur om hul geskiktheid te evalueer (Aanvullende Tabel S4). Genotipering is uitgevoer met behulp van die ekonomiese fluoresserende merkmetode waarin die M13-stert by elke voorwaartse SSR-onderlaag gevoeg word [56]. PCR-mengsels is voorberei in 20 gL-reaksie wat bevat: 50 ng totale DNA, 0.2 mM dNTP-mengsel, 1X PCR-reaksiebuffer, 0.8 E DreamTaq DNA-polimerase (Thermo Scientific, Waltham, MA, VSA), 0.16 gM omgekeerde onderlaag , 0.032 gM van voorwaartse primer verleng met die M13 volgorde (5'-TGTAAAACGACGGCCAGT-3'), en 0.08 gM van 'n universele M13 primer gemerk met FAM of NED fluoresserende kleurstowwe (Sigma-Aldrich, St. Louis, MO, VSA). Die PCR-reaksies is uitgevoer in die SimpliAmp (Applied Biosystems, CA, VSA) termosikleerder met die volgende toestande vir die meerderheid van die primer-pare: 94 °C vir 5 min, 40 siklusse by 94 °C vir 30 s, 58 °C vir 45 s en 72 °C vir 45 s en 'n finale verlenging by 72 °C vir 5 min. Soos vir ACM446 en ACM449, is 'n landing-PKR toegepas met uitgloeiing van 60 °C tot 55 °C oor 10 siklusse, 30 siklusse by 55 °C, gevolg deur 'n finale verlenging van 5 min by 72 °C. PCR produkte is in 'n 96-put plaat gelaai en gemeng met 14 gL Hi-Di Formamide (Life Technologies, Carlsbad, CA, VSA) en 0.5 gL GeneScan 500 ROX Size Standard (Life Technologies, Carlsbad, CA, VSA). Amplikone is opgelos deur middel van ABI PRISM 3100 Avant Genetiese Analiseerder (Life Technologies, Carlsbad, CA, VSA) kapillêre volgordebepalingsmasjien, waar die allele as mededominant aangeteken is en toegeken is deur die GeneMapper sagteware weergawe 3.7 te gebruik.
Die sagteware GenAlEx 6.5 [57] en Cervus 3.0.7 [58] is gebruik om die aantal allele (Na), die aantal effektiewe allele (Ne), waargenome heterosigositeit (Ho), verwagte heterosigositeit (He), polimorfiese inligtinginhoud (PIC), Shannon se inligtingsindeks (I) en fiksasie-indeks (Fis) te skat. ) vir elke SSR-lokus.
Assessering van genetiese diversiteit
Hiërargiese verdeling van genetiese variasie tussen en binne die uie populasies is geëvalueer deur GenAlEx 6.5 [57] deur die ontleding van molekulêre variansie (AMOVA) met 999 self-strapping om te toets vir betekenis. Boonop is GenAlEx 6.5-sagteware gebruik om die diversiteit binne elke populasie te skat deur die gemiddelde van Ho, He en Fis oor al die SSR-lokusse te bereken.
Bevolkingstruktuur is afgelei deur die Bayes-modelgebaseerde groeperingsalgoritme wat in die STRUCTURE v.2.3.4-sagteware geïmplementeer is [59]. Die datastel is uitgevoer met 'n aantal hipotetiese trosse (K), wat wissel van 1 tot 10, wat tien onafhanklike lopies per elke K-waarde stel. Vir elke lopie, met die doel om die konsekwentheid van resultate te verifieer, is 100,000 100,000 aanvanklike inbrandperiode en XNUMX XNUMX Markov Chain Monte Carlo (MCMC) iterasies uitgevoer onder die byvoegingsmodel en onafhanklike alleelfrekwensies onder populasies. Die mees waarskynlike K-waarde is bepaal deur die AK-metode, beskryf deur [60], in die webgebaseerde program STRUCTURE HARVESTER [61]. 'n Individuele populasie is aan 'n spesifieke groep toegewys wanneer sy lidmaatskapkoëffisiënt (q-waarde) hoër as 0.7 was, anders is dit as 'n gemengde afkoms beskou.
Hoofkoördinaatanalise is uitgevoer om patrone van genetiese verwantskap tussen toetredings te visualiseer wat deur die Nei se genetiese afstandmatriks geopenbaar is (Aanvullende Tabel S5). Gebaseer op alleelfrekwensies, is 'n dendrogram van genetiese afstand gekonstrueer deur die ongeweegde paargroepmetode met rekenkundige gemiddeldes (UPGMA)-klusteranalise in die POPTREEW-sagteware te implementeer [62]. Bootstrapping is toegepas om die vertroue in hiërargiese groepering te bepaal, wat 100 hermonstering van die datastel stel. Ten slotte, MEGA X sagteware [63] is as boomtekenprogrammatuur gebruik.
Aanvullende materiaal: Die volgende is aanlyn beskikbaar by http://www.mdpi.com/2223-7747/9/2/260/s1. Tabel S1: Morfologiese karakterisering van ARO-, MCO- en TRO-gloeilampe. Tabel S2: Heterosigositeit en fiksasie-indekse bereken vir ARO-landrasse en TRO- en MCO-landrasse. Tabel S3: Paarsgewyse waardes van die Fpt-parameter. Tabel S4: Lys van die SSR'e wat in die studie gebruik is. Tabel S5. Paarsgewyse populasiematriks van Nei genetiese afstand. Figuur S1: Lyngrafiek van K-waardes wat verander met Evanno se Delta K.
Skrywer Bydraes: CL en LR het die studie bedink en die eksperiment ontwerp; CL en PI het molekulêre merkeranalise uitgevoer; ARM en VZ het die veldproewe uitgevoer; RM, SP, GR en CL was betrokke by data-analise; RM en CL het die manuskrip geskryf. Alle skrywers het die gepubliseerde weergawe van die manuskrip gelees en daartoe ingestem.
befondsing: Hierdie werk is gefinansier deur die Streeks-Apuliese projek "Biodiversiteit van Apuliese groentespesies"—Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; toekenning CUP H92C15000270002, Italië.
Erkennings: Erkennings is te danke aan "Azienda Agricola Iannone Anna" en "Associazione produttori della vera cipolla rossa di Acquaviva" vir die verskaffing van plantmateriaal wat in die eksperiment gebruik is.
Botsings van belange: Die outeurs verklaar geen belangebotsing nie.
Verwysings
- 1. Stearn, WT Hoeveel spesies Allium is bekend? Kew Mag. 1992, 9, 180-182. [CrossRef]
- 2. FAOSTAT. FAO Statistiese Databasis. Aanlyn beskikbaar: http://www.fao.org/2017 (toegang op 8 Januarie 2019).
- 3. Blok, E. Die chemie van knoffel en ui. Wetenskap. Am. 1985, 252, 114-119. [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS Assessering van rooi ui op antioksidantaktiwiteit by rotte. Food Chem. Toksikool. 2012, 50, 3912-3919. [CrossRef]
- 5. Lee, SM; Maan, J.; Chung, JH; Cha, YJ; Shin, MJ Effek van quercetin-ryke uieskil ekstrakte op arteriële trombose by rotte. Food Chem. Toksikool. 2013, 57, 99-105. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. Anti-vetsug effekte van uie uittreksel in zucker diabetiese vetterige rotte. Voedingstowwe 2012, 4,1518-1526. [CrossRef]
- 7. Akash, MSH; Rehman, K.; Chen, S. Speseryplant Allium cepa: Dieetaanvulling vir behandeling van tipe 2-diabetes mellitus. Voeding 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y.; Tian, WX; Ma, XF Inhiberende effekte van ui (Allium cepa L.) uittreksel op proliferasie van kankerselle en adiposiete via inhiberende vetsuursintase. Asiatiese Pac. J. Kanker Vorige. 2012,13, 5573-5579. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Chueh, FS; Chen, JJ; Yang, JS; Lin, JP; Lien, JC; Tsai, CH; Chung, JG Quercetin inhibeer migrasie en indringing van SAS menslike mondkankerselle deur inhibisie van NF-kappaB en matriks metalloproteïnase-2/-9 seinweë. Antikanker Res. 2013, 33, 1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA Knoffel en uie: hul kankervoorkomingseienskappe. Kanker Vorige. Res. 2015, 8,181-189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M.; Bigi, A. Antioksidant- en beenhersteleienskappe van quercetin-gefunksionaliseerde hidroksiapatiet: 'n In vitro osteoblast-osteoklast-endoteliale sel-ko-kultuurstudie. Acta Biomater. 2016, 32, 298-308. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Verspreiding van elf geurvoorlopers, S-Alk(en)yl-L-sisteïenderivate, in sewe Allium-groente. Voedselwetenskap. Tegn. Res. 2011, 17, 55-62. [CrossRef]
- 13. Block, E. Die organoswaelchemie van die genus Allium—Implikasies vir die organiese chemie van swael. Angew. Chem. Int. Ed. Engl. 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Thomas, B.; Smith, B. Uie-'n Wêreldwye voordeel vir gesondheid. Fitoter. Res. 2002,16, 603-615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ Ensiematiese ontwikkeling van pirodruivensuur in ui as 'n maatstaf van skerpheid. J. Agric. Food Chem. 1961, 9, 301-304. [CrossRef]
- 16. Ketter, KAT; Randle, WM Skerpheidsbeoordeling in uie. In Getoetste Studies vir Laboratorium Onderrig; Karcher, SJ, Red.; Association for Biology Laboratory Education (ABLE): New York, NY, VSA, 1998; Jaargang 19, pp. 177-196.
- 17. Hanelt, P Taksonomie, evolusie en geskiedenis. In Uie en verwante gewasse, Vol. I. Plantkunde, Fisiologie en Genetika; Rabinowitch, HD, Brewster, JL, Eds.; CRC Press: Boca Raton, FL, VSA, 1990; pp. 1-26.
- 18. Rabinowitz, HD; Currah, L. Allium Crop Science: Onlangse vooruitgang; CABI Publishing: Wallingford, Verenigde Koninkryk, 2002.
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Karakterisering van genetiese hulpbronne van ui (Allium cepa L.) van Spaanse sekondêre sentrum van diversiteit. Span. J. Agric. Res. 2011, 9, 144-155. [CrossRef]
- 20. Ferioli, F.; D'Antuono, LF Evaluering van fenole en sisteïensulfoksiede in plaaslike uie en sjalot kiemplasma van Italië en Oekraïne. Genet. Hulpbron. Crop Evol. 2016, 63, 601-614. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Morfologiese, voedingswaarde en chemiese beskrywing van 'vatikiotiko', 'n plaaslike ui-landras uit Griekeland. Food Chem. 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratinni, F.; Di Matteo, M.; Albanese, D. Biochemiese, antioksidante eienskappe en antimikrobiese aktiwiteit van verskillende uievariëteite in die Mediterreense gebied. J. Food Meas. Karakter. 2019,13, 1232-1241. [CrossRef]
- 23. Yoo, KS; Snoek, L.; Crosby, K.; Jones, R.; Leskovar, D. Verskille in uie skerpheid as gevolg van kultivars, groei omgewing, en bol groottes. Wetenskap. Hortic. 2006,110, 144-149. [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; George, E.; Kroh, LW; Rohn, S. Verspreiding van quercetin-3, 4'-O-diglucoside, quercetin-4'-O-monoglucoside, en quercetin in verskillende dele van die uiebol (Allium cepa L.) beïnvloed deur genotipe. Food Chem. 2010,122, 566-571. [CrossRef]
- 25. Caruso, G.; Conti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Effekte van uitplanttyd en plantdigtheid op opbrengs, kwaliteit en antioksidantinhoud van ui (Allium cepa L.) in Suid-Italië. Wetenskap. Hortic. 2014,166, 111-120. [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF Die verhoging van die toegevoegde waarde van uie as 'n bron van antioksidante flavonoïede: 'n Kritiese oorsig. Crit. Eerw. Food Sci. Nutr. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweiggert, RM; Carle, R. Impak van verbouingsmetode en kultivarseleksie op oplosbare koolhidrate en skerp beginsels in uie (Allium cepa L.). J. Agric. Food Chem. 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I.; Carbone, V.; Spagnuolo, C.; Minasi, P.; Russo, GL Identifikasie en kwantifisering van flavonoïede van twee Suid-Italiaanse kultivars van allium cepa L., Tropea (rooi ui) en Montoro (koper ui), en hul vermoë om menslike eritrosiete teen oksidatiewe stres te beskerm. J. Agric. Food Chem. 2015, 63, 5229-5238. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. Hoë-deurset genotipering in uie openbaar struktuur van genetiese diversiteit en insiggewende SNP's wat nuttig is vir molekulêre teling. Mol. Ras. 2019, 395. [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F Genetiese variasie van 'n Italiaanse lang raklewe tamatie (Solanum lycopersicum L.) versameling deur gebruik te maak van SSR en morfologiese vrugte-eienskappe. Genet. Hulpbron. Crop Evol. 2014, 62, 721-732. [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Verkenning van genetiese diversiteit en kwaliteit eienskappe in 'n versameling van uie (Allium cepa L.) landrasse van Noordwes-Spanje. Genetika 2015, 47, 885-900. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo, C.; Pavan, S.; Ricciardi, L. Genetiese, bio-agronomiese en voedingskarakterisering van boerenkool (Brassica oleracea L. var. acephala) diversiteit in Apulië, Suid-Italië. Diversiteit 2018,1025. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. Genetiese analise van weerstand teen Orobanche crenata (Forsk.) in 'n ertjie (Pisum sativum L.) lae-strigolaktoon lyn. J. Plant Pathol. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Kartering van kwantitatiewe eienskap loci vir vasbouttyd in bos uie (Allium fistulosum L.). Euphytica 2016, 209, 537-546. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan, AK Identifikasie van geniese SSR's en konstruksie van 'n SSR-gebaseerde koppelingskaart in Brassica juncea. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Mote, SR; Gopal, J. Evaluering van uie variëteit identiteit met behulp van SSR merkers. Saad Sci. Tegnologie. 2014, 42, 279-285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. Die seleksie en validering van 'n merkerstel vir die differensiasie van uiekultivars uit die Tsjeggiese Republiek. Tsjeg J. Genet. Plantras. 2015, 51, 62-67. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. Die bewaring en karakterisering van Apuliese olyfkiemplasma-biodiversiteit. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. Assessering van die genetiese diversiteit van Spaans allium cepa landrasse vir uie teel met behulp van mikrosatelliet merkers. Wetenskap. Hortic. 2014,170, 24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Assessering van die genetiese diversiteit in uie (allium cepa L.) landrasse van Noordwes-Spanje en vergelyking met die Europese veranderlikheid. NZJ Crop Hortic. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G.; Montemurro, C.; Ricciardi, L.; Lotti, C. Genetiese variasie van 'n globale kiemplasmaversameling van kekerertjies (Cicer arietinum L.) insluitend Italiaanse toetredings met die risiko van genetiese erosie. Fisiol. Mol. Biol. Plante 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, R.; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti, C. Genetiese diversiteit in broccoli rabe (Brassica rapa L. subsp. sylvestris (L.) Janch.) van Suid-Italië. Wetenskap. Hortic. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M.; Martin, W.; McCallum, J.; Havey, M. Enkelnukleotied polimorfismes, indels, en eenvoudige volgorde herhalings vir uie kultivar identifikasie. J. Am. Soc. Hortic. Wetenskap. 2005,130, 912-917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. Genetiese diversiteitsanalise en enkel-nukleotied polimorfisme merker ontwikkeling in gekweekte bol ui gebaseer op uitgedrukte volgorde merker-eenvoudige volgorde herhaal merkers. J. Am. Soc. Hortic. Wetenskap. 2008,133, 810-818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Ontwikkeling van robuuste genomiese eenvoudige volgorde herhalingsmerkers vir die skatting van genetiese diversiteit binne en tussen bol ui (Allium cepa L.) bevolkings. Mol. Ras. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Skow, LC Mikrosatelliet merkers in wit stert takbokke. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. Iranse ui (Allium cepa L.) kultivars se reaksie op inteling depressie. Wêreld Appl. Wetenskap. J. 2010,11, 426-428.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Boudewyn, JP; Hardy, OJ Genetiese diversiteit van Niger-uie (Allium cepa L.) geassesseer deur eenvoudige volgordeherhalingsmerkers (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pavan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al. 'n Afsonderlike genetiese groepering in gekweekte kekerertjies soos geopenbaar deur genoomwye merker-ontdekking en genotipering. Plantgenoom 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; Marcotrigiano, AR; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotipering-deur-volgordebepaling van 'n spanspek (Cucumis melo L.) kiemplasmaversameling vanaf 'n sekondêre sentrum van diversiteit beklemtoon patrone van genetiese variasie en genomiese kenmerke van verskillende geenpoele. BMC Genom. 2017, 1859. [CrossRef]
- 51. Di Rienzo, V.; Sion, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. Genetiese vloei onder olyfbevolking binne die Middellandse See-bekken. Peer J. 2018, 6. [CrossRef]
- 52. Herder, LD; McLay, TG Twee mikroskaal protokolle vir die isolasie van DNA van polisakkariedryke plantweefsel. J. Plant Res. 2011,124, 311-314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Isolasie van plant-DNS uit vars weefsel. Fokus 1990,12, 13-14.
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; Martin, W.; Zewdie, Y.; McCallum, J.; Catanach, A.; Rutherford, P.; Wasbak, KC; Jenderek, M.; et al. 'n Unieke stel van 11,008 XNUMX uie-uitgedrukte volgorde-etikette openbaar uitgedrukte volgorde en genomiese verskille tussen die eensaadlobbige ordes asparagales en poales. Plantsel 2004,16, 114-125. [CrossRef]
- 55. Kim, HJ; Lee, HR; Hyun, JY; Lied, KH; Kim, KH; Kim, JE; Hur, CG; Harn, CH Merkerontwikkeling vir uie genetiese suiwerheidstoetsing met behulp van SSR Finder. Koreaans J. Ras. Wetenskap. 2012, 44, 421-432. [CrossRef]
- 56. Schuelke, M. 'n Ekonomiese metode vir fluoresserende etikettering van PCR-fragmente. Nat. Biotegnologie. 2000, 18, 233-234. [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse, PE GenAlEx 6.5: Genetiese analise in Excel. Bevolkingsgenetiese sagteware vir onderrig en navorsing: 'n opdatering. Bioinformatika 2012, 28, 2537-2539. [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC Hersiening van hoe die rekenaarprogram CERVUS genotiperingsfoute akkommodeer, verhoog sukses in vaderskaptoewysing. Mol. Ecol. 2007,16, 1099-1106. [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Verenigingskartering in gestruktureerde bevolkings. Am. J. Hum. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. Opsporing van die aantal groepe individue met behulp van die sagteware STRUKTUUR: 'n Simulasiestudie. Mol. Ecol. 2005,14, 2611-2620. [CrossRef]
- 61. Earl, D.; VonHoldt, B. STRUCTURE HARVESTER: 'n Webwerf en program vir die visualisering van STRUCTURE-uitset en die implementering van die Evanno-metode. Conserv. Genet. Hulpbron. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: Webweergawe van POPTREE vir die konstruksie van bevolkingsbome uit alleelfrekwensiedata en die berekening van 'n paar ander hoeveelhede. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; Li, M.; Knyaz, C.; Tamura, K. MEGA X. Molekulêre Evolusionêre Genetika Analise oor rekenaarplatforms. Mol. Biol. Evol. 2018, 35, 1547-1549. [CrossRef]